中国海洋湖沼学会主办。
文章信息
- 马爱军, 王新安, 孙志宾, 赵艳飞, 孙建华, 王广宁, 孟雪松, 刘圣聪, 张涛. 2016.
- MA Ai-Jun, WANG Xin-An, SUN Zhi-Bin, ZHAO Yan-Fei, SUN Jian-Hua, WANG Guang-Ning, MENG Xue-Song, LIU Sheng-Cong, ZHANG Tao. 2016.
- 红鳍东方鲀(Takifugu rubripes)三个不同群体的形态差异分析
- MORPHOLOGICAL VARIATIONS AMONG THREE DIFFERENT POPULATIONS OF TAKIFUGU RUBRIPES
- 海洋与湖沼, 47(1): 166-172
- Oceanologia et Limnologia Sinica, 47(1): 166-172.
- http://dx.doi.org/10.11693/hyhz20150300083
-
文章历史
- 收稿日期: 2015-03-19
- 收修改稿日期: 2015-05-13
2. 青岛海洋科学与技术国家实验室海洋生物学与生物技术功能实验室 青岛 266071;
3. 大连天正实业有限公司 大连 116000
2. Laboratory for Marine Biology and Biotechnology, Qingdao National Laboratory for Marine Science and Technology, Qingdao 266071, China;
3. Dalian Tianzheng Industrial Co. Ltd., Dalian 116000, China
红鳍东方鲀(Takifugu rubripes),隶属于鲀形目(Telraodontiformes)、鲀科(Tetradontidae)、东方鲀属(Takifugu),是具有海江洄游习性的底栖鱼类,主要分布在黄海、渤海和东海。红鳍东方鲀肉味鲜美,营养丰富,脂肪含量低,含有丰富的多种有益微量元素,是经济价值较高的鱼种之一(Aparicio et al,2002; Asakawa et al,2010)。近年来,红鳍东方鲀在我国大连、秦皇岛、唐山、天津等地区开始大量养殖,已成为我国沿海河豚渔业的主要养殖种类,随着养殖规模扩大,生长速度慢、产量低、发病率高等种质退化现象不断发生,加之种质不纯正、养殖技术不规范等现象,严重制约了红鳍东方鲀养殖业的发展。因此,培育出优质、高产的红鳍东方鲀新品种,并进行低毒养殖是我国河豚养殖产业可持续发展的需求。
对于动物的选择育种,育种基础群体遗传背景分析是育种工作的基础,它可以评估遗传育种的潜力,决定着选择育种所能取得的遗传进展,甚至育种工作的成败。动物育种基础群体遗传变异的研究目前主要利用分子生物学(徐成等,2001; 全迎春等,2006; Chistiakov et al,2009)和生物多元统计(马爱军等,2008; 王新安等,2008)的方法进行。有关红鳍东方鲀选育群体的遗传变异已有利用分子生物学对其进行研究(郝君等,2006; 万玉美等,2011),但通过生物多元统计的方法对其进行研究尚未见有报道。目前,本课题组正在开展红鳍东方鲀的良种选育研究,也利用微卫星DNA遗传多样性研究分析了所收集选育群体的遗传变异。本研究采用聚类分析、主成分分析和判别分析三种生物多元统计方法和单因子方差分析方法对红鳍东方鲀三个选育群体的遗传背景进行分析,以期为红鳍东方鲀良种选育工作提供基础资料。
1 材料与方法 1.1 材料来源本研究所用数据为3个不同群体的红鳍东方鲀生长性能测定资料。其中,大连天正实业有限公司人工养殖群体,记为R; 大连天正从日本引进的群体,记为J; 大连天正在黄海捕捞的野生群体,记为Y。不同群体的培育,维持各项养殖管理条件基本一致。分别对3个群体进行数据采集时,为消除个体规格差异对实验结果的影响,所采用数据的大小规格应尽量接近。观察样本的数量和规格见表 1。
| 群体 | 样本数 | 体长(cm) | 体质量(kg) | |||
| 范围 | 平均值 | 范围 | 平均值 | |||
| 日本(J) | 153 | 22—33 | 28.475±1.624 | 0.470—1.22 | 0.843±0.135 | |
| 野生(Y) | 169 | 21—35.5 | 30.979±1.985 | 0.327—0.970 | 0.892±0.109 | |
| 养殖(R) | 39 | 22—34 | 32.112±2.022 | 0.389—1.033 | 0.977±0.176 | |
实地随机抽样,逐尾用游标卡尺、直尺等测量工具测定3个不同群体的形态学性状。群体测量参数包括全长(TL)、体长(BL)、体高(BD)、头长(HL)、眼后头长(EH)、吻长(SL)、口宽(MW)、眼径(ED)、眼间距(IS)、尾柄长(CPL)、尾柄高(CPD)、尾柄宽(CPB)、体宽(BW)、头长+躯干长(HL+TR)、尾长(TA)、体周长1(BG1)(沿背鳍前环躯干长度)、体周长2(BG2)(沿胸鳍后环躯干长度)等17个形态性状(图 1),精确到0.01cm。
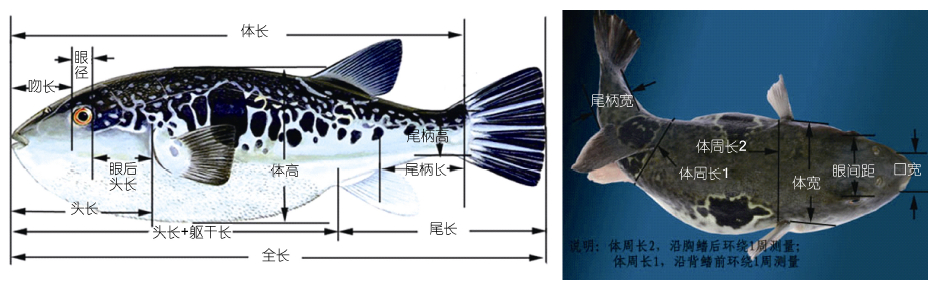 |
| 图 1 红鳍东方鲀形态学测量位点 Fig. 1 The morphological and mark points for measurement of T. rubripes |
对于上述所得的形态学特征数据与其体长(BL)的比值作为形态度量分析的性状值,以消除样本个体大小差异对形特征的影响(王新安等,2008)。共得到16个比例性状,采用统计软件SPSS11.5进行以下统计分析。
(1)聚类分析 参照等Betal等(2004)、钱荣华等(2003)的方法,利用软件分析所得欧几里德距离(Euclidean Distance)和相似系数(Coefficients)进行群体聚类,用树形图显示群体间的亲疏程度。
(2)主成分分析 参照Moralev(2001)、苏金明等(2002)的方法,通过软件分析,从所有参数指标中得出3个综合性指标,即3个主成分; 计算机软件分析将输出主成分1、主成分2和主成分3的贡献率及三者累积贡献率,显示各主成分的特征向量。
(3)判别分析 采用逐步分析(Use stepwisemethod)的方法对所有参数进行校正,对所有的样本进行逐个判别。判别准确率的计算公式:

(4)单因子方差分析 运用SPSS11.5软件,采用单因子方差分析(One-way ANOVA),并采用Duncan法进行组间多重比较分析不同群体间的形态差异。
2 结果与分析 2.1 聚类分析利用系统聚类分析,日本群体(J)、野生群体(Y)和养殖群体(R)间的平均欧式距离见表 2,聚类结果见图 2。从图 2可见: 日本群体(J)和养殖群体(R)先聚在一起,与养殖群体(R)一起被归为一类,然后再与日本群体(J)聚在一起,而日本群体(J)被归为另外一类。这说明野生群体(Y)与养殖群体(R)的形态较为相似。从表 2可见: 野生群体(Y)和养殖群体(R)的欧式距离为0.388839,与日本群体(J)的欧式距离为0.536764,养殖群体(R)和日本群体(J)间的欧式距离最大,为0.711762。
| 群体 | 日本群体(J) | 野生群体(Y) | 养殖群体(R) |
| 日本群体(J) | — | 0.536764 | 0.711762 |
| 野生群体(Y) | 0.536764 | — | 0.388839 |
| 养殖群体(R) | 0.711762 | 0.388839 | — |
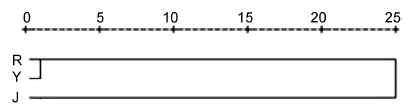 |
| 图 2 3个不同群体的聚类分析树形图 Fig. 2 Hierarchical dendrogram of three different populations of T. rubripes R. 养殖群体; Y. 野生群体2; J. 日本群体。下同 |
对红鳍东方鲀3个群体的16个形态比例性状进行主成分分析,共获得3个主成分。16个性状对3个主成分的特征向量及3个主成分的方差贡献率见表 3。结果表明: 第一个主成分贡献率为54.961%,根据主成分特征向量分量的绝对值可知,主要反映CPB/BL、CPD/BL、TA/BL、HL/BL、CPL/BL、BW/BL、MW/BL、BG2/BL、ED/BL和TR/BL等指标,其中CPB/BL、CPD/BL、TA/BL的影响最大; 第二个主成分贡献率为12.129%,明显比第一主成分低得多,主要反映BD/BL、IS/BL和TL/BL等指标; 第三个主成分更低,贡献率仅为6.459%,主要反映指标EH/BL。三个主成分的累积贡献率为73.549%,未达到累积贡献率大于或等于85%的要求,说明难以用几个相互独立的因子来概括红鳍东方鲀不同群体间的形态差异。
| 性状 | 主成分 | ||
| 1 | 2 | 3 | |
| BG1/BL | 0.744 | -0.004 | 0.105 |
| TL/BL | 0.011 | 0.728 | -0.399 |
| HL/BL | 0.986 | -0.041 | -0.057 |
| TR/BL | 0.934 | -0.082 | -0.086 |
| TA/BL | 0.990 | -0.002 | 0.030 |
| CPL/BL | 0.981 | 0.023 | 0.038 |
| SL/BL | 0.884 | -0.060 | -0.011 |
| EH/BL | 0.082 | 0.414 | 0.847 |
| ED/BL | 0.958 | -0.084 | 0.036 |
| CPD/BL | 0.991 | 0.006 | 0.045 |
| BD/BL | 0.166 | 0.902 | -0.106 |
| MW/BL | 0.966 | -0.110 | -0.082 |
| BW/BL | 0.967 | -0.066 | -0.023 |
| IS/BL | 0.239 | 0.860 | 0.022 |
| CPB/BL | 0.993 | -0.012 | 0.027 |
| BG2/BL | 0.966 | 0.012 | -0.058 |
| 各主成分贡献率(%) | 54.961 | 12.129 | 6.459 |
| 累积贡献率(%) | 54.961 | 67.090 | 73.549 |
用红鳍东方鲀3个不同群体的主成分1、主成分2和主成分3绘制三维空间主成分分析图,结果如图 3所示。主成分1主要反映了CPB/BL、CPD/BL、TA/BL、HL/BL、CPL/BL、BW/BL、MW/BL、BG2/BL、ED/BL和TR/BL等指标,主成分2主要反映了BD/BL、IS/BL和TL/BL等指标,而主成分3主要反映指标EH/BL。从图 3中可以看出: 3个群体间的形态差异分化明显,形成三个不同的类群,3群体在主成分1轴上的差异较在主成分2轴及主成分3轴上的差异明显。图中显示,野生群体(Y)和养殖群体(R)的形态差异较小,与日本群体(J)的形态差异稍大,养殖群体和日本群体(J)间的形态差异最大。
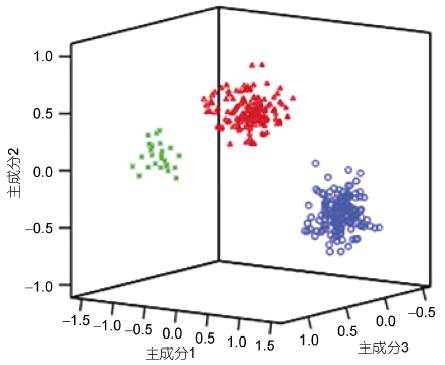 |
| 图 3 3个群体红鳍东方鲀主成分1、主成分2和主成分3的散布图 Fig. 3 Scatter diagram for PC1, PC2, and PC3 of Plot of T. rubripes form three different populations 蓝色(○)表示J; 红色(△)表示Y; 绿色(×)表示R |
利用逐步判别法,对16个形态比例参数进行判别分析。结果表明,除TA/BL和EH/BL两个比例性状外,其余14个比例性状依次进入判别公式,此时,判别准确率和综合判别率均为100%。显然,包含14个比例性状的判别公式对群体的判别是非常精确的,但同时工作量也很大,理想的判别公式应该既具有较高的判别率,又具有很强的实用性。因此,为了建立简便实用的判别公式,在确保一定判别准确率的前提下,进一步筛选出贡献较大的形态比例参数,并建立判别公式。从14个特征性状中筛选出对区分三类群体有显著贡献的6个变量,即IS/BL、TL/BL、BD/BL、ED/BL、BG2/BL和BW/BL进行判别分析,F检验的结果表明,这6个性状均达到极显著水平(P<0.01)。根据 6 个参数所建立的3个群体的判别公式为:

为验证判别公式的实用性,对测量样本按上述判别公式进行预测分类,见表 4。三个群体的判别准确率P1依次为99.33%、97.69%和100%,判别准确率P2依次为97.39%、100%和97.44%,综合判别率为98.62%。F检验结果表明判别效果较好(P<0.01),因此,群体的判别公式是可靠的。显然,对3个群体进行判别时,尽管包含6个比例性状的判别公式比包含14个性状的判别公式的准确率稍有降低,但各类判别率依然很高(>97.36%),同时工作量大大降低,因此可在实际工作中进行应用。要判断某尾红鳍东方鲀所归属的群体,只需测出上述6个形态比例参数,分别代入上述3个判别公式,计算出3个函数值,以函数值最大的判别函数所对应的群体名称作为该个体的群体名。
| 群体类型 | 预测分类 | 判别准确率 | 综合判别率(%) | |||
| J | Y | R | P1(%) | P2(%) | ||
| J | 149 | 0 | 1 | 99.33 | 97.39 | |
| Y | 4 | 169 | 0 | 97.69 | 100 | 98.62 |
| R | 0 | 0 | 38 | 100 | 97.44 | |
| 合计 | 153 | 169 | 39 | |||
| 百分率(%) | 42.38 | 46.81 | 10.80 | |||
对红鳍东方鲀3个群体的16个形态比例性状分别进行单因子方差分析,并对差异显著者在两两群体间进一步进行多重比较分析,分析结果见表 5。方差分析结果表明: 在群体间所比较的16个形态比例性状值中,除比例性状MW/BL差异不显著(P>0.05)外,其余均达到显著(P<0.05)或极显著水平(P<0.01)。两两比较结果表明: 养殖群体(R)和日本群体(J)之间差异显著的有15项,其中12项达到极显著水平; 养殖群体(R)和野生群体(Y)之间差异显著的有8项,其中6项达到极显著水平; 日本群体(J)和日野生群体(Y)之间差异显著的有13项,其中9项达到极显著水平。
| 性状 | J | Y | R |
| BG1/BL | 1.031±0.677AB | 0.701±0.025B | 0.774±0.075A |
| TL/BL | 1.173±0.009Aa | 1.151±0.194Ba | 1.220±0.040AB |
| HL/BL | 0.355±0.301ab | 0.298±0.065b | 0.276±0.022a |
| TR/BL | 0.380±0.324Ba | 0.514±0.167AB | 0.321±0.028Aa |
| TA/BL | 0.627±0.536AB | 0.346±0.084B | 0.333±0.027A |
| CPL/BL | 0.401±0.372AB | 0.140±0.040B | 0.183±0.021A |
| SL/BL | 0.140±0.126A | 0.128±0.154a | 0.090±0.009Aa |
| EH/BL | 0.172±0.080Aa | 0.148±0.050a | 0.140±0.008A |
| ED/BL | 0.043±0.037Aa | 0.034±0.022Ba | 0.017±0.001AB |
| CPD/BL | 0.215±0.183AB | 0.013±0.03B | 0.103±0.012A |
| BD/BL | 0.243±0.006AC | 0.200±0.040BC | 0.232±0.018AB |
| MW/BL | 0.127±0.110 | 0.119±0.048 | 0.105±0.007 |
| BW/BL | 0.348±0.292A | 0.397±0.093B | 0.235±0.030AB |
| IS/BL | 0.220±0.001AC | 0.184±0.031AC | 0.200±0.012AB |
| CPB/BL | 0.227±0.201AB | 0.148±0.030B | 0.119±0.015A |
| BG2/BL | 0.860±0.738Ba | 0.396±0.100AB | 0.660±0.054Aa |
目前,动物群体差异分析主要有分子生物学(徐成等,2001; 全迎春等,2006; Chistiakov et al,2009)和生物多元统计(马爱军等,2008; 王新安等,2008)两种方法。由于实验材料易得,操作简便,生物多元统计方法近年来得到广泛应用(钱荣华等,2003; 马爱军等,2008; 王新安等,2008; 李义军等,2010; 董志国等,2010)。具体来说,多元统计就是研究客观事物中多个变量(或多个因素)之间相互依赖的统计规律性,它的重要基础之一是多元正态分析,又称多元分析。近年来,随着统计理论研究的不断深入,多元统计分析方法的内容一直在丰富。其中,主要内容包括多元正态总体参数估计、假设检验和常用的多元统计方法。多元正态总体参数估计、假设检验是多元统计推断的核心和基础,而常用的多元统计分析方法则是具体应用。从形式上,常用多元统计分析方法可划分为两类: 一类属于单变量常用的统计方法在多元随机变量情况下的推广和应用,如多元回归分析、典型相关分析等; 另一类是对多元变量本身进行研究所形成的一些特殊方法,如主成分分析、因子分析、聚类分析、判别分析、对应分析等。在动物领域,通常利用主成分分析、聚类分析和判别分析对群体差异进行综合判定(钱荣华等,2003; 马爱军等,2008; 王新安等,2008; 李义军等,2010; 董志国等,2010)。
本文利用聚类分析、主成分分析和判别分析三种常用的生物多元统计方法以及单因子方差分析的方法对3个不同群体红鳍东方鲀的形态差异进行了研究。聚类分析是对不同群体进行初步归类,量化群体间的差异程度,常被用来对分析对象的相似程度进行分析(蔡庆华,1990; 李勤生等,1991)。本研究中,从聚类分析树形图和群体间的欧式距离可以看出,3个不同群体的红鳍东方鲀群体间,日本群体(J)和养殖群体(R)的差异最大,野生群体(Y)和养殖群体(R)的差异最小,野生群体(Y)和日本群体(J)的差异处于中间位置。主成分分析是一种将原来多个彼此相关的指标转换为新的、个数较少且相互独立或不相关综合指标的方法,可以化简为繁,且不损失或很少损失原有信息,在体型分析中已得到广泛应用(钱荣华等,2003; 魏开建等,2003)。将多个形态比例性状综合成少数几个因子,从而得出不同群体的差异大小,并可根据不同群体的主成分值找出各群体在各主成分值上差异较大的参数(钱荣华等,2003; 韩冰等,2007)。在本研究中,从主成分分析图上可以看出,3个不同群体的红鳍东方鲀群体,形态差异分化明显,形成三个不同的类群,野生群体(Y)和养殖群体(R)的形态偏离较小,与日本群体(J)的形态偏离稍大,养殖群体(R)和日本群体(J)间的形态偏离最大。这与聚类分析的结果相同。判别分析是鉴定鱼类群体的常用方法之一,用构建的判别公式可以较准确地进行群体的判别(练青平等,2011)。在本研究的判别分析中,利用贡献率最大的6 个参数IS/BL、TL/BL、BD/BL、ED/BL、BG2/BL和BW/BL构建了3个判别函数,对3 种鱼样本的综合判别准确率为98.62%,错判率仅为1.38%。显然,本函数的判别效果较好。进一步观察发现,进入判别函数的贡献率最大的3个参数IS/BL、TL/BL、BD/BL是主成分分析中主成分2所反映的指标,另3个贡献率大的参数ED/BL、BG2/BL和BW/BL是主成分1所反映的指标。对红鳍东方鲀3个群体的16个形态比例性状方差分析多重比较的结果表明,养殖群体(R)和日本群体(J)之间差异显著的有15项,其中12项达到极显著水平; 养殖群体(R)和野生群体(Y)之间差异显著的有8项,其中6项达到极显著水平; 日本群体(J)和野生群体(Y)之间差异显著的有13项,其中9项达到极显著水平,显然,从方差分析的结果可以看出,养殖群体(R)和日本群体(J)之间差异最大,养殖群体(R)和野生群体(Y)之间差异最小。综合3种生物多元统计分析和方差分析的结果可以看出,方差分析与聚类分析、主成分分析和判别分析的结论基本上是类似的,但也存在稍许差异,它们从不同的角度反映了群体间的形态学差异,其作用是不可相互替代的。
事实上,基于生物多元统计的方法对动物群体差异进行研究,想要得到精确的结果并非一项容易的工作。这主要是由于动物群体尺寸规格的差异会使研究结论失真,出现“假分离”现象。为消除群体大小差异对研究结果的影响,通常情况下,采用所采集的形态特征数据与其体长的比值作为形态度量分析的性状值,本文也对分析数据进行了这种处理。然而,这种转换方法也只是在一定程度上减弱了群体差异对研究结果的影响,因为即使是对相同的动物群体,在不同发育阶段的表型形态的比值范围也是不同的。因此,利用生物多元统计研究不同动物群体差异的良好方法,是在尽量缩小不同群体大小规格差异的前提下,同时采用生物多元统计和分子生物学的方法对相同的研究对象进行研究,即: 分子生物学的研究材料来源于生物多元统计的研究个体,对两种研究结论综合分析,得出较为准确的结论。
| 万玉美,王蕾,谭照君等,2011.红鳍东方鲀两个群体的遗传结构及与经济性状的相关性分析.淡水渔业, 41(5):9-16 |
| 马爱军,王新安,雷霁霖等,2008.大菱鲆(Scophthalmus maximus)四个不同地理群体数量形态特征比较.海洋与湖沼, 39(1):24-29 |
| 王新安,马爱军,陈超等,2008.七带石斑鱼(Epinephelus septemfasciatus)两个野生群体形态差异分析.海洋与湖沼, 39(6):655-660 |
| 全迎春,李大宇,曹鼎辰等,2006.微卫星DNA标记探讨镜鲤的种群结构与遗传变异.遗传, 28(12):1541-1548 |
| 苏金明,傅荣华,周建斌等,2002.统计软件SPSS系列应用实战篇.北京:电子工业出版社, 290-301 |
| 李义军,李婷,王平等,2010.日本囊对虾(Marsupenaeus japonicus)3个野生种群和1个养殖种群的形态差异与判别分析.海洋与湖沼, 41(4):500-504 |
| 李勤生,蔡庆华,华俐等,1991.东湖异养细菌群落的分类结构和聚类分析.水生生物学报, 15(3):242-253 |
| 练青平,宓国强,胡廷尖等,2011.唇鱼骨、花鱼骨及其杂交F1的形态差异分析.大连海洋大学学报, 26(6):493-499 |
| 郝君,孙效文,孟雪松,2006.红鳍东方鲀微卫星DNA多态性初步分析.上海水产大学学报, 15(1):21-24 |
| 钱荣华,李家乐,董志国等,2003.中国五大湖三角帆蚌形态差异分析.海洋与湖沼, 34(4):436-443 |
| 徐成,王可玲,张培军,2001.鲈鱼群体生化遗传学研究Ⅱ.种群生化遗传结构及变异.海洋与湖沼, 32(3):248-254 |
| 董志国,李晓英,阎斌伦等,2010.中国海五种群三疣梭子蟹的形态差异分析.海洋通报, 29(4):421-426 |
| 韩冰,王艳君,高天翔,2007.黄、东海3个黄姑鱼群体和1个鱼群体的形态学比较研究.海洋水产研究, 28(3):23-30 |
| 蔡庆华,1990.武汉东湖浮游植物水华的多元分析.水生生物学报, 14(1):22-31 |
| 魏开建,熊邦喜,赵小红等,2003.五种蚌的形态变异与判别分析.水产学报, 27(1):13-18 |
| Aparicio S, Chapman J, Stupka E et al,2002. Whole-genome shotgun assembly and analysis of the genome of Fugu rubripes. Science, 297(5585):1301-1310 |
| Asakawa M, Fujita Y, Yasui K et al,2010. Anthelmintic effects of excitatory amino acids in red algae for parasitic copepods of cultured pufferfish. In:Aquaculture 2010-Meeting. San Diego, California:The World Aquaculture Society, 136 |
| Betal S, Chowdhury P R, Kundu S et al,2004. Estimation of genetic variability of Vigna radiate cultivars by RAPD analysis. Biologia Plantarum, 48(2):205-209 |
| Chistiakov D A, Voronova N V,2009. Genetic evolution and diversity of common carp Cyprinus carpio L. Central European Journal of Biology, 4(3):304-312 |
| Moralev S N,2001. Cholinesterase active center statistical analysis of structure variability. Journal of Evolutionary Biochemistry and Physiology, 37(1):25-34 |
 2016, Vol. 47
2016, Vol. 47

